Escaneando la biodiversidad mundial, un fragmento de ADN a la vez
Irina Formoso

Por miles de años los humanos hemos clasificado la vida que nos rodea. Primero para saber qué comer o de qué huir y posteriormente por curiosidad, lo que daría origen a naturalistas y taxónomos. A pesar de tener 250 años de estudio y clasificación formal de las especies, se estima que más del 80% de ellas no han sido descritas, porcentaje mayor aún al considerar organismos como las bacterias. Y es que la taxonomía es una ciencia que requiere paciencia, tiempo y mucha atención al detalle, con una pizca de suerte durante la colecta de los especímenes.
Organismos grandes y carismáticos como aves y mamíferos son más fáciles de conseguir e identificar, por lo que se encuentran descritos en detalle. Pero ¿qué hacer con organismos que hasta en un microscopio son muy pequeños? ¿Qué ocurre cuando decenas de hongos se parecen, aunque sean de especies diferentes? ¿Cómo podemos identificar animales que imitan los patrones de colores de otras especies? Problemas como estos hacen que las estimaciones de biodiversidad en la Tierra tengan una gran variabilidad, y que, a pesar de ya haber identificado más de 1,7 millones de organismos, quizás existan muchos más sin identificar escondidos dentro de esa cifra y millones de especies desconocidas en áreas remotas del planeta.

De la forma a los genes
El desarrollo del secuenciador de ADN en los años 70 fue una nueva oportunidad para entender la biodiversidad en un nuevo plano, pues añadía un componente molecular a los caracteres físicos utilizados en la taxonomía tradicional. Sin embargo, su aplicación para entender el árbol de la vida es limitada ya que, aún en los secuenciadores más modernos, analizar el ADN completo de una gran cantidad de muestras sigue siendo costoso y requiere mucho tiempo.
Además, a medida que el curso de la vida evolucionó en diferentes especies sus genomas también fueron cambiando, por lo que no siempre el mismo método molecular funciona para todos los grupos y se requiere entonces diseñar nuevos métodos para extraer la información genética apropiada. Ante la amenaza evidente de la pérdida de diversidad, necesitábamos un método para monitorear poblaciones no sólo eficiente en costos y tiempo, sino que además se pudiese estandarizar para una gran cantidad de especies. Y así es como a principios de este siglo nació una idea que revolucionó el campo de la taxonomía y el estudio de la biodiversidad.
El código de barras del ADN
Paul Herbert, un biólogo molecular de la Universidad de Guelph, Canadá, y su equipo propusieron en 2003 un método que sirve como un código de barras en el ADN (DNA Barcoding), que al «escanearlo» se supiera fácilmente a qué especie pertenece.
Al estar en un supermercado verás que cada producto tiene su propio código de barras. Todas las leches de la marca A tendrán el mismo código, pero será diferente al de la marca B. Gracias a este código, se sabe exactamente qué producto estás comprando y de qué marca es. De igual forma que no es necesario leer toda la caja de leche al pagar sino sólo su código de barras, se buscaba sólo un pedacito de todo el genoma que te diera la información necesaria para saber si era la especie A o la B. En este caso, en vez de tener barras y números como lenguaje del código, se utilizan combinaciones de las cuatro letras que constituyen el ADN de todos los seres vivos: A, T, G, y C.
Hasta el momento no se ha encontrado una región del genoma que funcione para todos los organismos. Un genoma está conformado por el ADN de diferentes organelos de una célula (como núcleo, mitocondrias, plásmidos y ribosomas), y a pesar de tener muchas similitudes entre organismos, nuestros genomas pueden ser muy distintos en cuanto a tamaño, tipos de genes, organelos que aportan ADN, y muchas otras cualidades.
Además de estas diferencias, la región a utilizar como código de barras debe cumplir ciertos requisitos: debe ser de longitud corta para analizarse rápido, ser abundante para poder tener muchas copias, y debe ser posible de extraer en muchos organismos con las mismas herramientas moleculares. Todo esto suma dificultades para conseguir la región adecuada, problema que se resolvió usando regiones diferentes para cada grupo.
En el caso de los animales se utiliza un gen que proviene de las mitocondrias llamado COI, mientras que en hongos es la región ITS de los ribosomas, y en plantas, siempre tan complejas, la información proviene de varias regiones del ADN de plásmidos y ribosomas. Pero ¿cómo se obtiene este código de barras?
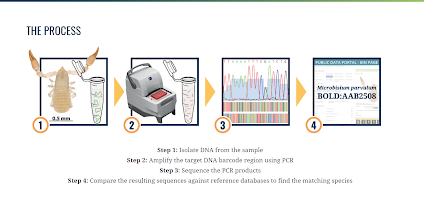
En la figura se observa un pseudoescorpión del cual queremos saber su especie. Como primer paso debemos tomar una muestra de tejido, y utilizando diferentes químicos, separamos el ADN completo del resto del material de la célula sin destruirlo. Luego se extrae la región de código de barras del ADN, en este caso el gen COI, mediante varios reactivos químicos y el método de la PCR, tan famoso en estos tiempos de pandemia.
Nuestro tercer paso será usar un secuenciador para leer nuestro código; en nuestro ejemplo se lee la combinación TTAAAATTTCGATCTG. Por último registramos y comparamos este código con una base de datos, para finalmente identificar a qué especie corresponde.
He allí el gran reto de esta increíble herramienta: para poder usarla en toda su capacidad, es necesario construir primero una gigantesca base de datos con el código de barras de cada especie. Como una gran enciclopedia genética de la vida, es necesario añadir fascículo por fascículo hasta completarla. Y es precisamente esa la labor que lleva actualmente el Consorcio Internacional del Código de Barras de la Vida (iBOL por sus siglas en inglés), un ambicioso trabajo en el que más de 35 países contribuyen a la base de datos, entre ellos representantes latinoamericanos como Argentina, México y Perú. Para el 2015 se logró recopilar en la base de datos medio millón de especies identificadas, y se espera alcanzar 2.5 millones de especies en 2,000 localidades para el año 2026.
Más allá del registro de especies
En 2003, un hombre en Brasil viajaba con 58 huevos de supuestas codornices. Las autoridades sospechaban que podía ser un caso de tráfico de especies protegidas, pero al ser huevos era casi imposible identificar a qué especie pertenecían. El sujeto fue liberado a los pocos días de su aprehensión pagando la multa mínima.
Años después, un equipo de la Universidad de São Paulo utilizó el código de barras de ADN en los mismos huevos, y determinaron que era un caso de tráfico ilegal de loros y guacamayas. En este tipo de crímenes, las condenas dependen del estado de conservación y protección de las especies, por lo que de tener esta evidencia a mano ayudaría a tener casos legales sólidos y penalizaciones adecuadas, y ayudaría a monitorear qué especies son las más perseguidas.
Lo anterior es un ejemplo de cómo esta herramienta tiene una gran utilidad en la conservación de especies. También se puede aplicar en otros ámbitos legales como el control de calidad y fraude en el etiquetado de productos alimenticios, o en investigaciones policiales donde sea necesaria la entomología forense para estimar tiempos de post mortem. De la misma forma se puede beneficiar la salud humana, al detectar y comprender los complejos ciclos de vida de parásitos y sus vectores de transmisión.
En el ámbito ambiental facilita el monitoreo de ecosistemas para estudios sobre contaminación y cambio climático, ayudando a entender mejor el impacto antropogénico en la Tierra. Además, la detección temprana y monitoreo de especies invasoras permitirá reducir sus impactos en el ecosistema y en la economía. Si bien el entendimiento y clasificación de la biodiversidad ya son razones suficientes para realizar un proyecto de esta magnitud, existen numerosas aplicaciones donde el código de barras de ADN sin duda tendrá un papel importante.
El Consorcio Internacional del Código de Barras de la Vida demuestra cómo el avance tecnológico y la inversión gubernamental para conocer la biodiversidad puede acelerar y mejorar a gran escala una disciplina centenaria. Más importante aún, nos recuerda que ante la presencia de una gran colaboración científica internacional no existen proyectos demasiado grandes.
Para saber más
- International Barcode of Life Project: https://ibol.org/
- Catalogue of Life https://www.catalogueoflife.org/
- Mora C, Tittensor DP, Adl S, Simpson AGB, Worm B. (2011). How many species are there on Earth and in the ocean? PLOS Biology 9: e1001127.
- Hebert PDN, Cywinska A, Ball SL, deWaard JR. (2003). Biological identifications through DNA barcodes. Proceedings of the Royal Society of London: Biological Sciences 270: 313–321
- Chimeno C, Moriniere J, Podhorna J, et al. DNA barcoding in Forensic Entomology – Establishing a DNA Reference Library of potentially forensic relevant arthropod species. Journal of Forensic Sciences: doi: 10.1111/1556-4029.13869.
- Galimberti A, De Mattia F, Losa A, et al. (2013). DNA barcoding as a new tool for food traceability. Food Research International 50: 55-63.
- Shehata HN, Naaum AM, Garduño RA, Hanner R. (2018). DNA barcoding as a regulatory tool for seafood authentication in Canada. Food Control 92: 147 – 153.
- Fišer Pečnikar ZF, Buzan EV. (2014). 20 years since the intoduction of DNA barcoding: from theory to application. Journal of Applied Genetics: doi: 10.1007/s13353-013-0180-y.
- Gonçalves PFM, Oliveira-Marques AR, MatsumotoTE, Miyaki CY. (2015). DNA Barcoding Identifies Illegal Parrot Trade. Journal of Heredity 106: 560–564.
 Irina Formoso es Licenciada en Biología, Universidad Simón Bolívar, Venezuela y Master en Ecología, Evolución y Sistemática, Universidad de Múnich Ludwig-Maximilians, Alemania. Actualmente es Asistente de Investigación en el Colección estatal Zoológica de Múnich. Irina ha sido divulgadora científica en Famelab Germany, La SVE va la escuela y ¿Por qué ciencias? Mantiene el blog en inglés sobre ecología: Curiosity Seeds. Twitter: @Irinagorila
Irina Formoso es Licenciada en Biología, Universidad Simón Bolívar, Venezuela y Master en Ecología, Evolución y Sistemática, Universidad de Múnich Ludwig-Maximilians, Alemania. Actualmente es Asistente de Investigación en el Colección estatal Zoológica de Múnich. Irina ha sido divulgadora científica en Famelab Germany, La SVE va la escuela y ¿Por qué ciencias? Mantiene el blog en inglés sobre ecología: Curiosity Seeds. Twitter: @Irinagorila
AGRADECIMIENTOS
Fundación Persea agradece la infinita generosidad de sus patrocinadores Estrella Roja: Sobella Mejías, Solmar Valera, Leonardo Quevedo, My fit body project y Cristhian De Castro.
